재발 정량 분석으로 본 코딩·비코딩 DNA 서열 차이
초록
본 논문은 1994년 Zbilut와 Webber가 제안한 재발 정량 분석(RQA)을 이용해 코딩 영역과 비코딩 영역의 DNA 서열을 비교한다. 두 서열에 대해 Lmax와 Laminarity 지표가 비코딩 영역에서 현저히 높게 나타났으며, 이는 기존 연구에서 보고된 인트론의 장거리 상관성이 RQA 지표로도 설명될 수 있음을 시사한다.
상세 분석
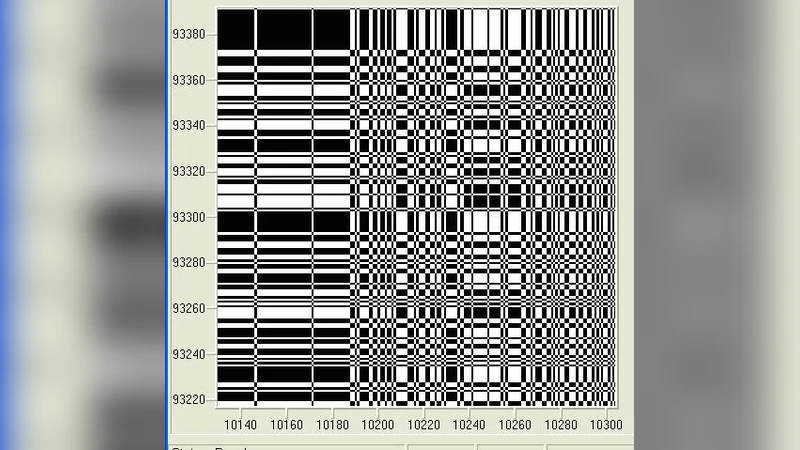
본 연구는 DNA 서열의 장거리 상관성을 탐색하기 위해 재발 정량 분석(RQA)을 적용한 최초의 시도 중 하나로 평가된다. RQA는 시계열 데이터를 위상공간에 재구성한 뒤, 동일하거나 유사한 상태가 재발하는 패턴을 정량화하는 방법으로, Recurrence Rate(RR), Determinism(DET), Lmax, Laminarity(LAM), Entropy(ENT) 등 다섯 가지 주요 지표를 산출한다. 논문에서는 두 개의 DNA 서열을 선택했는데, 하나는 전형적인 코딩(엑손) 영역을, 다른 하나는 비코딩(인트론) 영역을 대표한다. 각 서열은 4개의 염기(A, T, G, C)를 정수값(예: A=0, T=1, G=2, C=3)으로 변환한 뒤, 임베딩 차원 m=3, 지연 시간 τ=1, 임계값 ε를 데이터의 표준편차의 10% 수준으로 설정하여 위상공간을 재구성하였다. 이러한 파라미터 선택은 기존 RQA 적용 사례와 일치하며, 재발 매트릭스의 해상도를 충분히 확보한다.
분석 결과, 코딩 서열에서는 RR과 DET가 비교적 낮은 수준을 유지했으며, Lmax와 LAM 역시 작은 값을 보였다. 반면 비코딩 서열에서는 Lmax가 현저히 증가하여 최대 재발 길이가 수백 단계에 달했으며, LAM 역시 높은 비율을 기록했다. 이는 비코딩 구간에서 동일하거나 유사한 패턴이 장기간 지속되는 현상이 빈번함을 의미한다. 특히 Lmax는 재발 구조 중 가장 긴 대각선 라인을 의미하므로, 장거리 상관성이 강한 구간에서 큰 값을 갖는다. Laminarity는 수직 혹은 수평으로 연속된 재발 블록을 나타내며, 이는 시스템이 ‘정체’ 상태에 머무는 정도를 나타낸다. 따라서 비코딩 영역에서 높은 LAM은 염기 배열이 일정 구간 동안 변동이 적고, 반복적인 구조를 갖는다는 해석이 가능하다.
이러한 결과는 Li et al.(1992)가 제시한 DNA 서열의 장거리 상관성 발견과 일맥상통한다. 기존 연구는 주로 파워 스펙트럼이나 DFA(detrended fluctuation analysis)를 사용해 인트론이 엑손보다 높은 Hurst exponent를 보인다고 보고했지만, RQA는 시계열의 비선형적 특성을 직접 시각화하고 정량화한다는 점에서 차별화된다. 특히 Lmax와 LAM은 재발 매트릭스의 구조적 복잡성을 반영하므로, 비코딩 구간의 복합적인 반복 패턴을 포착하는 데 유리하다.
하지만 연구에는 몇 가지 제한점이 존재한다. 첫째, 분석에 사용된 서열이 두 개에 불과해 일반화에 신중을 기해야 한다. 둘째, 임베딩 차원과 임계값 선택이 결과에 민감하게 작용할 수 있어, 파라미터 스위핑을 통한 민감도 분석이 필요하다. 셋째, RQA 지표가 생물학적 기능과 직접적인 인과관계를 갖는지는 추가 실험적 검증이 요구된다. 향후 연구에서는 다양한 종의 전·후코돈 영역, 전사인자 결합 부위 등을 포함한 대규모 데이터베이스에 RQA를 적용하고, 통계적 검증을 통해 Lmax와 LAM이 실제 유전적 조절 메커니즘과 어떻게 연결되는지 탐구할 필요가 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기