테더드 파티클 모션 실험 정밀 보정
초록
본 논문은 DNA 길이와 비드 크기에 따른 테더드 파티클 모션(TPM) 신호를 정량적으로 보정하고, 영상 획득 시간·노출 시간 등 실험 파라미터가 측정값에 미치는 영향을 체계적으로 분석한다. 200 bp~2.6 kbp의 DNA와 200 nm, 490 nm, 970 nm 비드 직경을 이용해 RMS 변위와 이론 모델을 비교함으로써 TPM 데이터 해석의 정확성을 크게 향상시킨다.
상세 분석
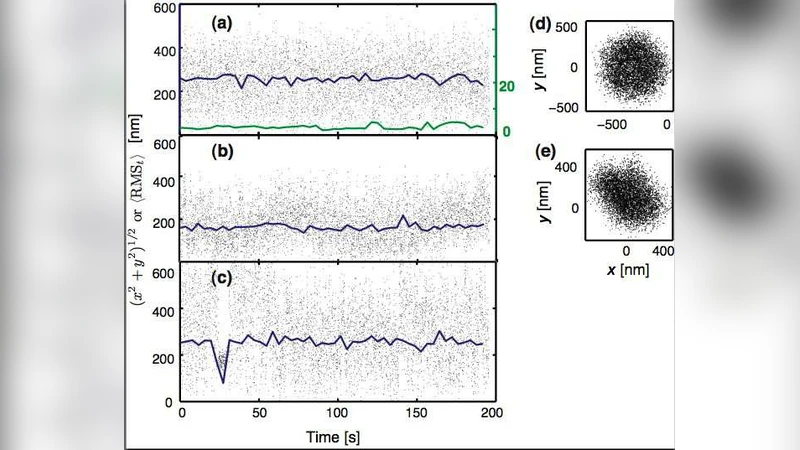
이 연구는 TPM 실험에서 가장 기본이 되는 ‘입자 변위(RMS)’를 물리적 파라미터와 직접 연결시키는 정밀 보정 작업을 수행한다. 먼저 저자들은 비드가 유리 표면에 고정되거나 다중 테더가 결합된 경우를 배제하기 위해 ‘최소 변위’, ‘변위 대칭성’, ‘시간적 균일성’이라는 세 가지 자동 선택 기준을 도입하였다. 최소 변위 기준은 30 nm 이하의 RMS를 보이는 비드를 제거함으로써 고정된 비드를 걸러내고, 대칭성 기준은 공분산 행렬의 고유값 비율(λ_max/λ_min ≤ 1.1)을 이용해 비대칭 궤적을 식별한다. 마지막으로 균일성 기준은 전체 측정 시간을 10개의 구간으로 나누어 각 구간의 RMS 평균값의 표준편차(u) 를 전체 평균 RMS로 정규화한 뒤 u < 0.2 인 경우만을 채택한다. 이러한 전처리 과정을 거치면 전체 데이터의 약 50 %만이 고품질 TPM 궤적으로 남으며, 이는 비드가 실제 DNA 테더에 의해 자유롭게 움직이고 있음을 보장한다.
다음으로 저자들은 윈도우 시간(t) 선택이 RMS 추정에 미치는 영향을 실험적으로 조사하였다. 비드의 확산 시간 τ_diff 은 비드 반경과 DNA 길이에 비례적으로 증가하므로, 짧은 t(≤ 2 s)에서는 비드가 충분히 탐색하지 못해 RMS가 과소평가되고, 긴 t(≥ 30 s)에서는 시간 해상도가 떨어진다. 실험에서는 200 s 동안 데이터를 수집하고, t = 5 s(200 nm 비드), 10 s(490 nm 비드), 20 s(970 nm 비드) 를 ‘안전한’ 윈도우로 정의하였다. 이때 평균 RMS는 t가 증가함에 따라 포화값에 수렴하고, 표준편차는 감소하는 경향을 보였다. 이는 비드의 확산이 완전히 평형에 도달했을 때 측정값이 안정된다는 물리적 직관과 일치한다.
핵심 보정 결과는 비드 직경과 DNA 길이에 따른 RMS‑L 관계이다. 실험적으로 얻은 RMS 값은 200 nm, 490 nm, 970 nm 비드 각각에 대해 200 bp~2.6 kbp 구간에서 측정되었으며, 각 데이터셋에 대해 2차 다항식 RMS = a L² + b L + c 로 피팅하였다. 표 1에 제시된 계수는 비드가 클수록 a와 b가 크게 양의 값을 갖고, c는 작은 음수 값을 보여 비드 크기가 클수록 같은 DNA 길이에서도 변위가 크게 감소함을 의미한다. 또한 4 s 윈도우로 측정한 RMS는 ‘안전한’ 긴 윈도우에 비해 체계적으로 낮게 나타났으며, 이는 실험적 윈도우 선택이 민감도에 직접적인 영향을 미친다는 점을 강조한다.
마지막으로 저자들은 실험 RMS와 기존 이론 모델(예: Worm‑Like Chain 기반의 자유 에너지 최소화 모델) 사이의 차이를 비교하였다. 실험값은 이론값보다 약 5 %~15 % 정도 낮게 측정되었는데, 이는 비드와 표면 사이의 미세한 반발력, 비드 표면에 부착된 잔류 DNA 조각, 그리고 비드 자체의 회전 자유도 등이 추가적인 제약을 가하기 때문으로 해석한다. 이러한 차이를 정량화함으로써 향후 TPM 데이터를 해석할 때 ‘보정된’ RMS‑L 곡선을 적용하면 루프 형성, DNA 굽힘, 단백질 결합에 따른 미세한 길이 변화를 10 nm 이하의 정밀도로 감지할 수 있다.
전반적으로 이 논문은 TPM 실험의 핵심 측정값을 물리적 파라미터와 직접 연결시키는 정밀 보정 프레임워크를 제공하며, 데이터 전처리, 윈도우 선택, 비드‑DNA 상호작용에 대한 이해를 통합함으로써 단일분자 수준의 DNA‑단백질 상호작용 연구에 필수적인 정량적 도구를 제시한다.
댓글 및 학술 토론
Loading comments...
의견 남기기