핵심 유전체 탐색 종간 유전체 유사성 분석
초록
본 연구는 세 개의 Shewanella 균주 전장 유전체를 이용해 상동 유전자를 전산적으로 탐색하고, 상호 블라스트(Reciprocal BLAST) 분석을 통해 모든 균주에 공통으로 존재하는 68개의 보존 유전자를 식별하였다. 이들 유전자는 대부분 세포 기본 기능을 담당하는 하우스키핑 유전자로, 핵심 유전체(core genome) 개념을 실증적으로 뒷받침한다. 향후 인간·침팬·마카크와 같은 포유류 간에도 동일한 방법을 적용할 수 있음을 제시한다.
상세 분석
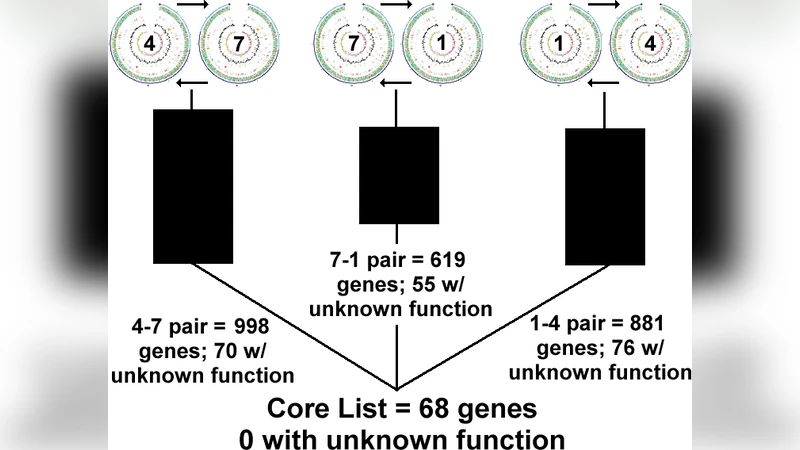
이 논문은 ‘핵심 유전체(core genome)’라는 개념을 실증적으로 검증하기 위해, 근연 세균인 Shewanella 속의 세 균주(세 개의 전장 유전체)를 대상으로 전산적 비교 분석을 수행하였다. 먼저 각 유전체에서 ORF를 예측하고, 이를 전부 단백질 서열 데이터베이스로 구축하였다. 이후 Reciprocal BLAST(상호 블라스트) 전략을 적용했는데, 이는 A 유전체의 각 ORF를 B, C 유전체에 BLAST하고, 반대로 B, C 유전체의 ORF를 A 유전체에 BLAST함으로써 양방향에서 최고 일치(hit)를 확인하는 방식이다. 이 과정에서 E‑value, 정렬 길이, 동일성(percentage identity) 등 엄격한 필터링 기준을 설정해 false positive를 최소화하였다. 초기에는 수천 개의 후보 유전자가 도출되었으나, 양방향 일치와 동일성 기준을 모두 만족하는 경우에만 최종 후보군에 포함시켰다. 결과적으로 68개의 유전자가 세 균주 모두에서 완전 일치하는 것으로 확인되었다.
이 68개의 보존 유전자는 기능적 주석(annotation)을 통해 대부분이 DNA 복제, 전사, 번역, 세포벽 합성, 대사 경로 등 기본적인 세포 유지에 필수적인 하우스키핑 유전자로 분류되었다. 이는 ‘핵심 유전체’가 진화적으로 보존된 필수 기능을 담당한다는 기존 가설을 강력히 지지한다. 또한, 논문은 이러한 접근법이 박테리아뿐 아니라 포유류, 특히 인간·침팬·마카크와 같은 근연 종 사이에서도 적용 가능하다고 제안한다. 포유류의 경우 유전체 크기와 복잡성이 크게 증가하므로, 고성능 컴퓨팅 자원과 효율적인 파이프라인 설계가 필요하지만, 기본 원리는 동일하다.
기술적 관점에서 이 연구는 몇 가지 중요한 시사점을 제공한다. 첫째, 전장 유전체 수준에서의 상호 블라스트는 대규모 데이터셋에서도 높은 정확도를 유지할 수 있는 실용적인 방법이다. 둘째, 필터링 기준을 명확히 정의함으로써 ‘보존 유전자’와 ‘우연히 일치하는 유전자’를 구분할 수 있다. 셋째, 기능적 주석을 결합함으로써 생물학적 의미를 부여하고, 단순히 서열 일치에 그치지 않는 통합적 해석이 가능해진다. 이러한 접근법은 미생물 군집 메타게놈 분석, 병원성 유전자 탐색, 그리고 진화적 계통수 구축 등 다양한 분야에 확장 적용될 수 있다.
마지막으로, 논문은 향후 연구 방향으로 (1) 더 많은 종을 포함한 광범위한 핵심 유전체 정의, (2) 유전자의 발현 수준과 기능적 중요성을 결합한 다층적 분석, (3) 진화적 압력과 선택 압력에 따른 보존 정도의 정량적 모델링 등을 제시한다. 이러한 연구는 종 간 유전체 비교를 통한 진화 생물학적 통찰을 제공하고, 핵심 유전체를 기반으로 한 새로운 바이오마커 개발 및 합성 생물학적 설계에도 기여할 수 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기