물리 기반 DNA 시퀀싱 혁신
초록
본 논문은 기존 화학·광학 기반 시퀀싱과 달리, 나노채널·나노포어와 같은 물리적 구속을 이용해 DNA를 단일 염기 수준에서 탐지하는 여러 방법을 리뷰한다. 각 접근법의 물리 원리, 장점·한계, 그리고 향후 연구 과제를 심도 있게 논의한다.
상세 분석
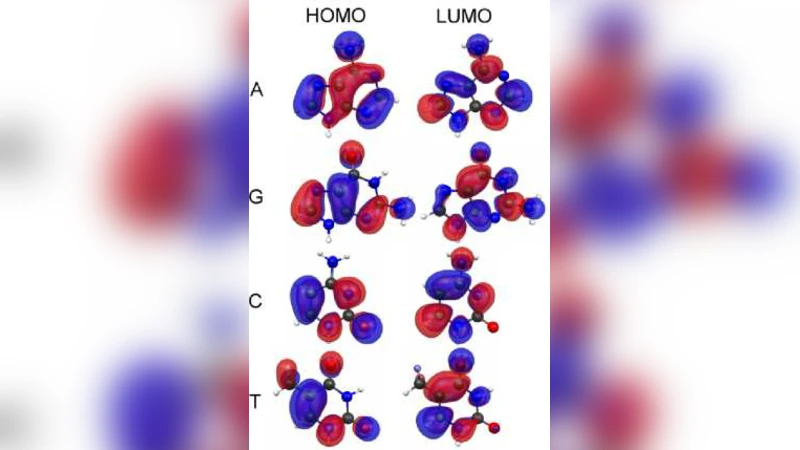
이 리뷰는 DNA 시퀀싱을 위한 물리적 접근법을 크게 네 가지 범주로 구분한다. 첫 번째는 전기적 신호를 이용하는 나노포어 기술이다. 단일 분자 DNA가 전도성 막에 형성된 나노스케일 구멍을 통과할 때, 전류 차단 현상이 발생한다. 염기마다 전하 밀도와 부피가 달라 전류 감소 폭이 변하므로, 이를 고속 전류 측정으로 해석하면 염기 서열을 추정할 수 있다. 그러나 전류 잡음, 포어 표면 전하 변동, 그리고 염기 간 전류 차이의 미세함이 현재 정확도를 제한한다. 두 번째는 나노채널 내에서 DNA를 물리적으로 늘려 광학 또는 전자 현미경으로 직접 관찰하는 방법이다. 채널 직경을 DNA 직경 이하로 설계하면 분자는 일직선으로 정렬되며, 형광 라벨 없이도 전자 현미경의 전자 투과 신호 혹은 광학 회절 패턴을 통해 염기 특성을 구분한다. 이 경우 라벨링이 필요 없다는 장점이 있지만, 채널 제작 공정의 복잡성 및 DNA‑채널 상호작용에 의한 변형이 문제로 남는다. 세 번째는 전극을 DNA 양쪽에 배치해 전자 터널링 전류를 측정하는 횡단 전류 방식이다. 터널링 전류는 전극 간 거리와 전자 파동함수 겹침에 민감해, 단일 염기의 전자밀도 차이를 실시간으로 감지한다. 현재는 전극 간 거리 제어와 전극 표면의 원자 수준 평탄화가 핵심 과제로 지적된다. 네 번째는 DNA를 기계적으로 끌어당겨 힘-거리 곡선을 측정하는 광학 트랩·AFM 기반 방법이다. 염기마다 결합 강도가 미세하게 다르므로, 힘 신호의 변화를 통해 서열을 추정한다. 이 방식은 높은 신호‑대‑노이즈 비를 제공하지만, 측정 속도가 느리고 복잡한 데이터 해석이 필요하다. 전반적으로 물리적 접근법은 비용 절감과 고속화를 목표로 하지만, 신호 감도, 잡음 억제, 그리고 대량 데이터 처리라는 공통된 과제가 존재한다. 향후 연구는 나노구조의 정밀 제어, 고감도 전자·광학 센서 개발, 그리고 머신러닝 기반 신호 해석을 결합해 현재의 한계를 극복하는 방향으로 진행될 것으로 전망된다.
댓글 및 학술 토론
Loading comments...
의견 남기기