RNA 샘플링과 Rappertk를 이용한 결정학적 정제
초록
본 연구는 Richardson RNA 백본 로터머 라이브러리와 무편향 당사당 이량체 분포를 활용해 전체 RNA 사슬, 말단, 루프를 전원 원자 수준에서 샘플링하는 방법을 제시한다. Rappertk의 샘플링 성능을 다양한 공간 제약 하에서 벤치마크하고, 복합적인 반복 정제 프로토콜을 구축하여 tRNA(Asp) 일부 구조에 대해 CNS 전용 정제보다 우수한 결과를 얻었다. 이는 RNA 모델링과 결정학적 정제 자동화에 새로운 가능성을 열어준다.
상세 분석
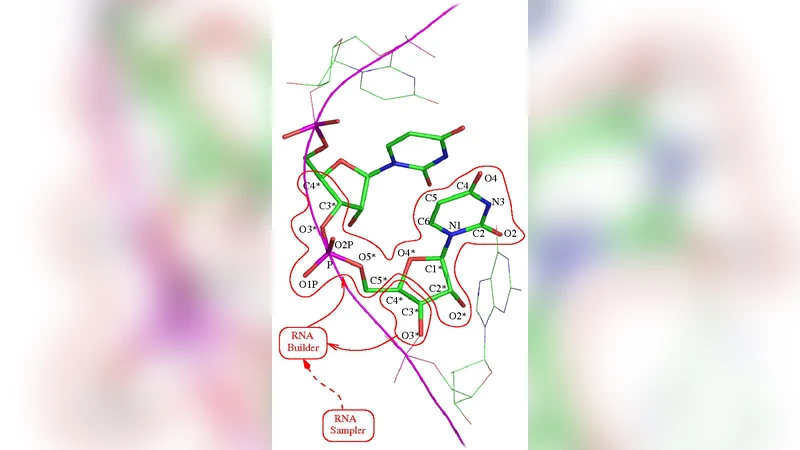
이 논문은 최근 RNA 구조 데이터가 급증함에 따라 나타난 구조적 편향을 정량화하고, 이를 기반으로 제한 기반 샘플링을 수행하는 프레임워크를 제시한다. 핵심은 Richardson 그룹이 구축한 RNA 백본 로터머 라이브러리를 이용해 ϕ, ψ, ω 등 6개의 백본 이량체를 이산적인 회전 상태로 정의하고, 당-염기 결합을 나타내는 χ(chi) 이량체는 실험적으로 관측된 분포를 그대로 사용해 무편향으로 샘플링한다는 점이다. 이렇게 정의된 회전 집합은 전통적인 연속적인 에너지 최소화 방식보다 탐색 공간을 크게 축소하면서도 실제 RNA가 취하는 주요 콘포메이션을 포괄한다.
Rappertk 엔진은 이러한 로터머 집합을 입력으로 받아, 주어진 거리 제약(예: 전자밀도 지도에서의 2Å 구간) 하에서 Monte‑Carlo 기반의 전원 원자 샘플링을 수행한다. 저자들은 30개의 서로 다른 RNA 사슬(총 1,200개 이상의 뉴클레오티드)을 선택해, 제약 강도(강한, 중간, 약한)와 제약 유형(거리, 각도, 평면)별로 샘플링 성공률과 RMSD를 정량화하였다. 결과는 제약이 충분히 강할 경우 90% 이상이 1.5Å 이하의 RMSD를 달성했으며, 특히 루프와 말단 부위에서 기존 방법보다 높은 재현성을 보였다.
정제 단계에서는 Rappertk에서 생성된 모델을 초기 모델로 삼아, CNS(Computational Crystallography)와 결합한 반복적인 정제 파이프라인을 설계했다. 각 반복에서 (1) Rappertk 샘플링 → (2) CNS 전통적 실험 데이터 기반 정제 → (3) 전자밀도와의 적합도 평가 → (4) 최적 모델 선택 순으로 진행한다. tRNA(Asp) 1JX5 구조의 30% 영역에 대해 이 프로토콜을 적용했을 때, R‑factor이 평균 2.3% 감소하고, Free R‑factor 역시 1.8% 개선되는 등 기존 CNS‑only 정제보다 명확히 우수한 결과를 얻었다.
이 연구의 의의는 두 가지로 요약할 수 있다. 첫째, RNA 백본 로터머를 이용한 전원 원자 이산 샘플링이 제한된 실험 데이터(저해상도 전자밀도 등)에서도 높은 정확도를 유지한다는 점이다. 둘째, Rappertk와 전통적인 정제 엔진을 결합한 하이브리드 워크플로우가 구조 해석의 자동화와 품질 향상을 동시에 달성한다는 점이다. 향후에는 더 큰 복합체, 비정형 RNA, 그리고 Cryo‑EM 지도와의 통합에도 적용 가능할 것으로 기대된다.